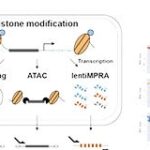
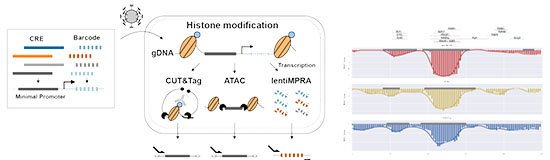
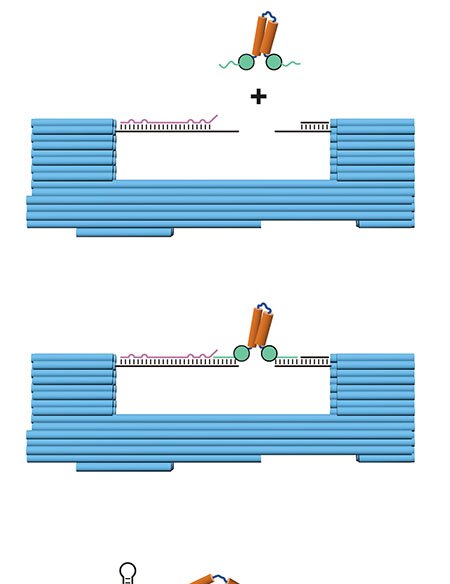
Cientistas do Instituto para o Estudo Avançado de Biologia Humana (WPI-ASHBi), da Universidade de Kyoto, apresentaram uma técnica que analisa, de uma só vez, como pequenas variações em sequências regulatórias de DNA influenciam a atividade gênica e o estado epigenético. Batizada de e2MPRA, a ferramenta avalia simultaneamente expressão de genes, acessibilidade da cromatina e a marca química H3K27ac, considerada sinal de regiões ativas.
O trabalho, liderado por Zicong Zhang e pelo professor associado Fumitaka Inoue, foi publicado em 23 de fevereiro de 2026 na revista Nature Communications. A equipe examinou cerca de 10 000 elementos cis-regulatórios (CREs) e suas variantes, segmentos de DNA que funcionam como “chaves” para ligar ou regular genes.
Como funciona o e2MPRA
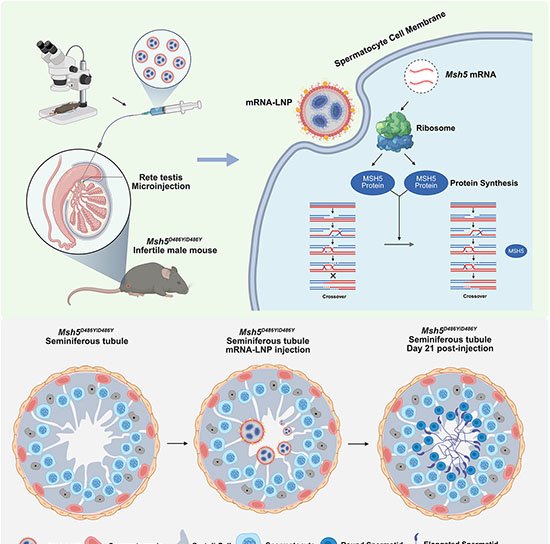
A técnica expande a plataforma lentiMPRA, que usa códigos de barras de DNA para rastrear a atividade de milhares de sequências em paralelo. O avanço do e2MPRA está em acoplar, no mesmo experimento, a leitura da atividade regulatória a perfis de cromatina e de modificações histônicas.
Para validar o método, os pesquisadores criaram duas bibliotecas: uma com CREs sintéticos contendo diferentes combinações de sítios de ligação para fatores de transcrição e outra com CREs conhecidos submetidos a mutações pontuais. Cada sequência foi medida em três aspectos: intensidade de ativação gênica, grau de abertura do DNA e presença da marca H3K27ac.
Principais resultados
Os testes mostraram que diferentes CREs atuam por mecanismos distintos. Alguns aumentam a atividade de genes sem alterar significativamente a estrutura do DNA, enquanto outros afetam principalmente a acessibilidade da cromatina. A ordem e a disposição dos sítios de ligação dentro de um CRE também se mostraram decisivas para sua função.

Imagem: Internet
Em sequências que contêm o motivo POU5F1::SOX2, essencial para manter a identidade de células-tronco, mutações reduziram a expressão gênica e modificaram tanto a acessibilidade do DNA quanto os níveis de H3K27ac. Já em regiões com sítios YY1, alterações diminuíram a atividade de genes, mas curiosamente aumentaram a abertura da cromatina, indicando que as variantes podem influenciar múltiplas camadas regulatórias de modo não linear.
Perspectivas
Segundo os autores, o e2MPRA cria uma base para investigar como diferenças individuais no DNA afetam características físicas e risco de doenças. Embora a versão atual examine segmentos curtos e não capture a organização tridimensional do genoma, o grupo planeja ampliar a técnica para estudos mais complexos.
Com informações de Nanowerk